南湖新闻网讯(通讯员 胡悦 贾宇鹏)在我们日常食用的菜籽油背后,隐藏着一个异常复杂而精妙的基因调控世界。作为全球重要的油料作物,油菜(Brassica napus)绝非“简单”的植物——它是由白菜和甘蓝两个祖先二倍体物种自然杂交形成的典型多倍体物种,其基因组由两套高度相似却又存在差异的亚基因组共同构成,分别是来自白菜的An亚基因组与来自甘蓝的Cn亚基因组。这样的“基因加倍”在为作物带来丰富遗传多样性和改良潜力的同时,也显著提高了基因表达调控的复杂性,使原本以线性基因组为基础的调控模式,演变为一个跨染色体、跨亚基因组高度耦合的调控体系。在此背景下,一个长期困扰科学界的重要问题逐渐凸显:这些分布在不同染色体、甚至不同亚基因组中的同源基因,究竟是如何实现协同调控,从而在发育过程中实现高度一致甚至同步表达的?
在多倍体生物中,由全基因组复制或杂交产生的大量同源基因往往成对存在,它们不仅分布在不同染色体上,甚至跨越不同亚基因组,却常常参与相同或相近的生物学过程,并呈现出显著的共表达特征。这种现象类似于分处不同空间的“协同系统”,在没有直接物理连接的情况下却能够保持高度一致的运行节奏。传统研究多从DNA序列相似性或局部顺式调控元件角度进行解释,但越来越多研究表明,仅依赖序列保守性难以充分解释这种跨尺度的表达协调现象,从而引出一个更深层的问题,即是否存在一种跨染色体乃至跨亚基因组的共享调控机制,使多个同源基因能够在更高层级上实现协同调控。
2026年4月7日,麻豆 杨庆勇教授课题组在国际期刊Genome Biology 发表题为“Profiling the transcriptional regulatory network reveals putative shared regulatory elements within homoeologs in polyploid Brassica napus”的研究论文。该研究以四倍体油菜为研究对象,通过整合多组学数据构建全基因组转录调控网络,在此基础上提出并系统验证了“同源基因共享调控元件”的新机制,从网络结构与空间组织两个层面,为理解多倍体基因表达协同提供了关键证据。

具体而言,研究团队整合染色质可及性(ATAC-seq)、DNA甲基化以及表达数量性状位点(eQTL)等多维度数据,在全基因组范围内系统鉴定了38,068个油菜种子时期的调控元件(Regulatory elements, REs),并筛选出其中24,541个具有遗传效应的调控元件,同时建立了包含791,512个RE–基因关联的调控网络。这一高分辨率网络相当于构建了一张覆盖油菜种子发育关键阶段的“全基因组调控地图”,不仅刻画了调控元件与基因之间的复杂关系,也为后续深入解析跨染色体调控提供了重要的数据基础。
在对调控网络进行系统分析的过程中,研究发现一个具有重要生物学意义的现象:在以同源基因对为靶标的调控关系中,大量共表达的同源基因对往往受到一个或多个相同的调控元件调控,即存在“共享调控元件”的模式。进一步比较表明,共享调控元件的同源基因对,其共表达水平显著高于未共享调控元件的同源基因对。这一结果提示,同源基因之间的共表达,并不仅仅来源于基因本身的序列特征,而在很大程度上受到上游调控元件的影响。
围绕这一关键发现,研究进一步引入三维基因组学数据进行解析,揭示了其潜在的空间结构基础。分析结果表明,染色质在细胞核中的空间邻近性,是驱动跨染色体同源基因共享调控元件的重要因素。尽管这些基因在线性基因组中相距较远,但在三维空间中可能相互靠近,从而使同一调控元件能够同时作用于多个基因,实现跨染色体调控。进一步在排除序列保守性影响后发现,这种由空间结构驱动的调控效应依然显著存在,说明三维基因组结构在多倍体基因表达协调中具有独立且不可替代的作用。
在此基础上,研究提出了三种由空间邻近驱动的跨染色体同源基因共享调控元件的理论模型,其中模型1占比最高(48,040,占54.89%),模型2次之(36,491,占41.70%),模型3所占比例较低(2,981,占3.41%)。在全基因组范围内,共鉴定到5,390组同源基因对(占所有同源基因对的7.34%)参与共享调控,涉及13,208个调控元件(占总REs的34.70%),表明这一机制在油菜基因组中具有广泛分布,而非偶发事件(图1)。这不仅从数量层面验证了共享调控的普遍性,也进一步凸显了其在多倍体基因调控中的关键作用。
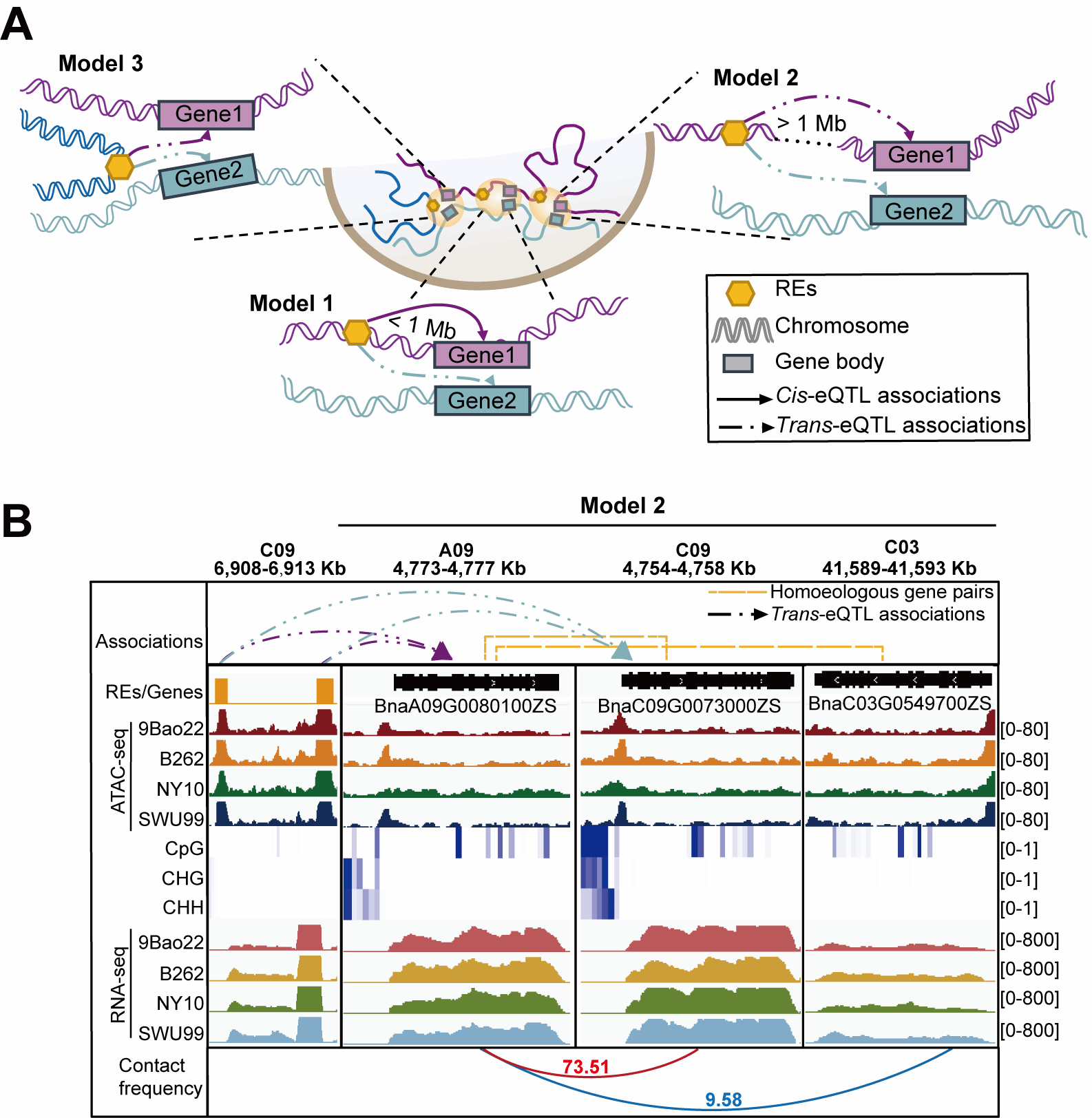
图1 空间邻近促使跨染色体同源基因对共享调控元件
除了共享调控机制外,研究还系统分析了调控网络在两个亚基因组之间的结构差异。结果显示,An亚基因组在网络中的节点数量、连接关系以及多种拓扑指标(如最大团中心性、边缘渗透分量和接近中心性)均高于Cn亚基因组,提示其在整体调控网络中处于更加核心的位置(图2A-B)。通过随机删除节点的模拟实验发现,在相同扰动条件下,Cn亚基因组网络完整度由94.50%下降至51.75%,而An亚基因组则由85.27%下降至2.61%,表明An亚基因组在维持网络整体结构中更接近“骨架”角色(图2C)。进一步分析指出,这种主导性主要来源于其独特的网络拓扑结构,而非单纯由节点数量差异所致。
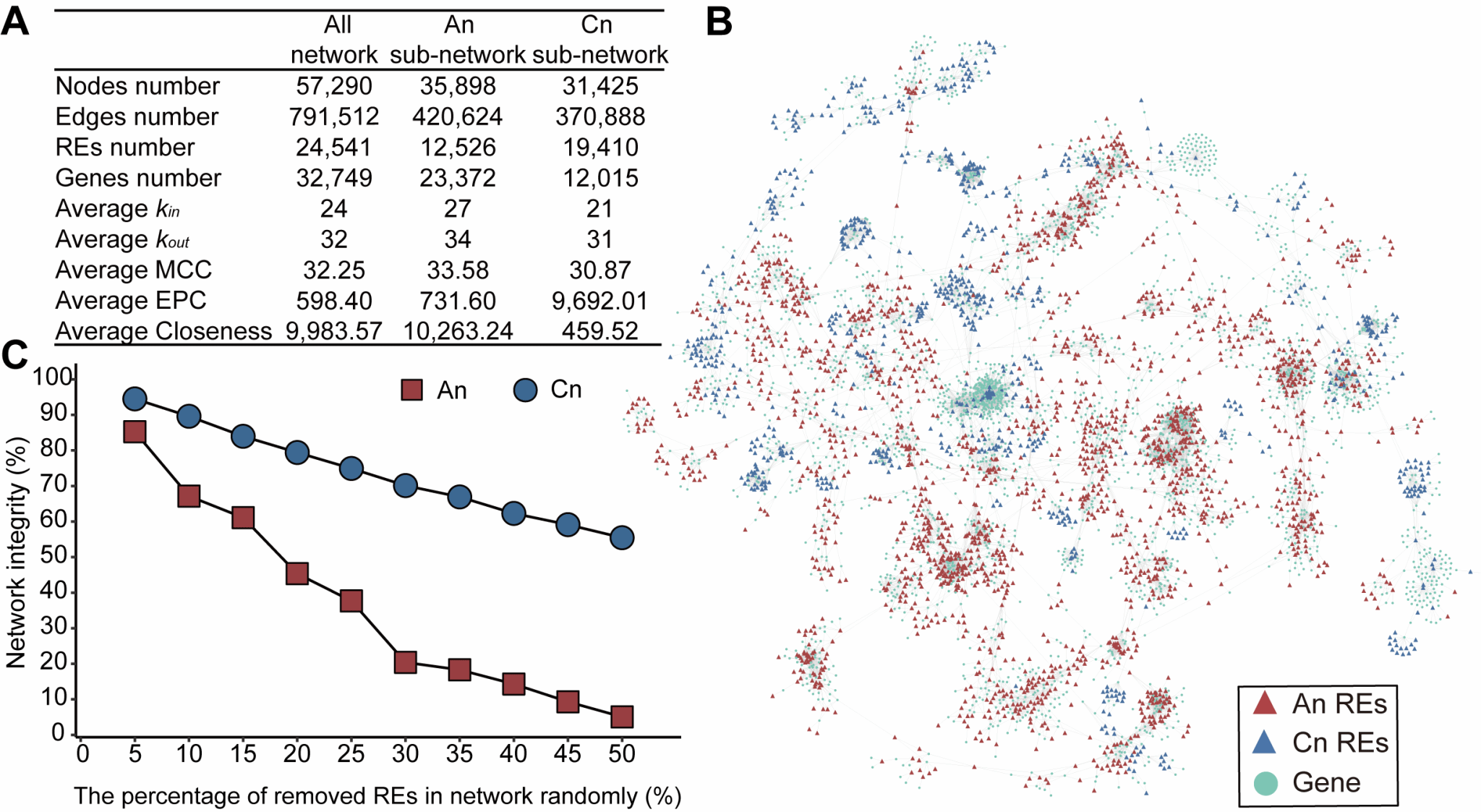
图2 油菜转录调控网络特征分析
与此同时,调控元件在亚基因组之间的分布及其作用也呈现出明显不对称性。来源于An亚基因组的调控元件(REAn)在数量上略高于Cn(12,526 vs. 12,015),在参与的调控关系数量(420,624 vs. 370,888)及调控强度方面均表现更高水平。在跨亚基因组调控中,An来源调控元件的参与比例更高(86.68% vs. 67.11%);进一步分析表明,REAn调控Cn基因(REAn→GCn)对应靶基因的表达水平显著高于RECn→GAn(图3)。这些结果共同揭示,多倍体油菜中存在显著的亚基因组调控不对称现象,而这种不对称性在很大程度上由调控元件的分布与作用差异所驱动。
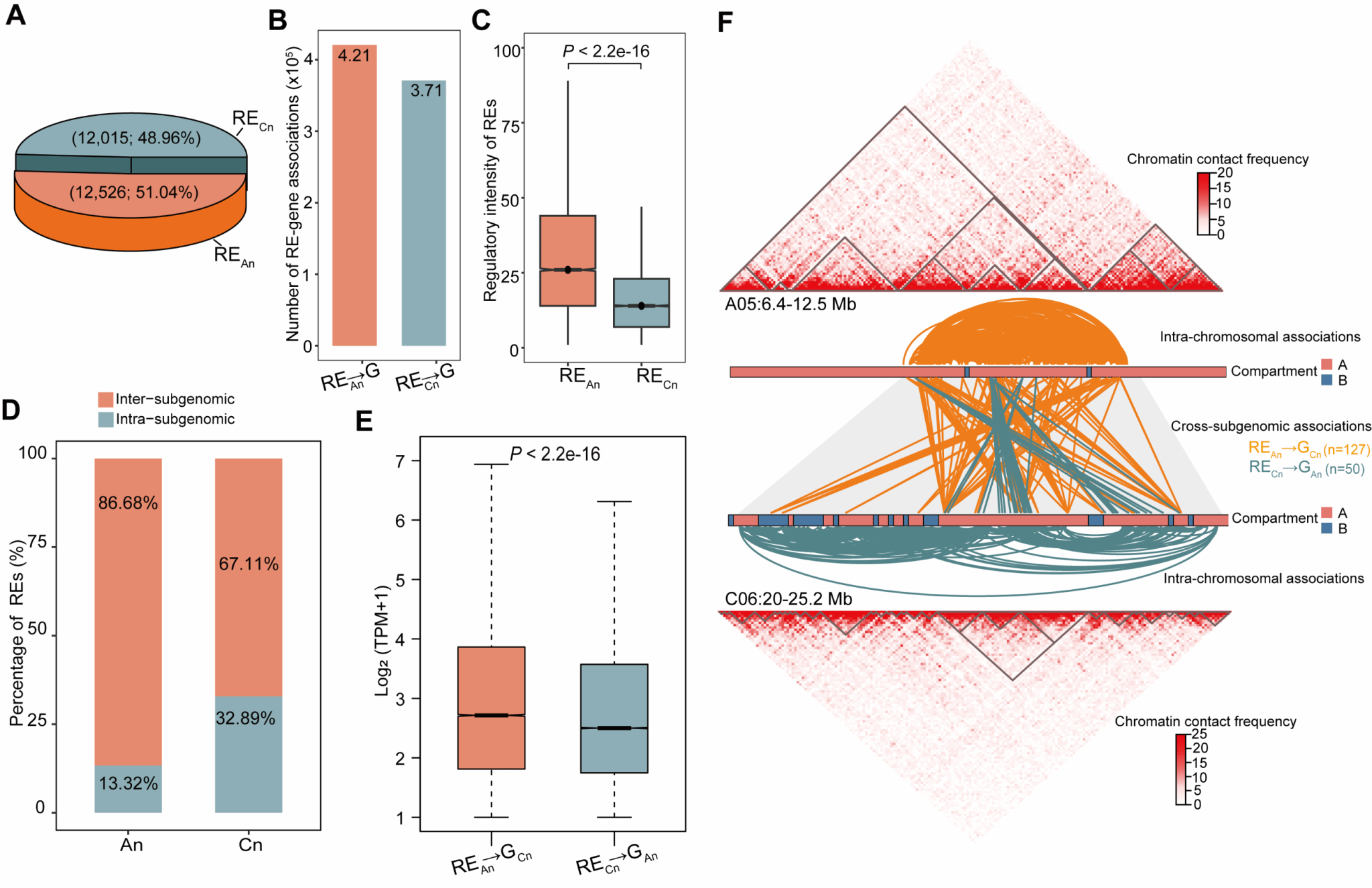
图3 RE-基因关联的不对称性分布有助于亚基因组调控不对称
该研究通过构建高分辨率调控网络,并结合三维基因组空间信息,从多个层面系统揭示了多倍体中同源基因协同表达的潜在机制,提出了“共享调控元件+空间邻近驱动”的新型调控模型。这不仅为解析油菜这一重要油料作物的复杂调控体系提供了关键资源,也为理解小麦、棉花等多倍体作物中的基因表达调控提供了可借鉴的理论框架。从更广泛的角度看,该研究提示,在复杂基因组背景下,基因调控需要从传统的“线性序列视角”拓展至“空间基因组视角”,这对于未来作物分子设计育种及复杂性状的精准调控具有重要启示意义。
麻豆 教授、崖州湾国家实验室主任科学家杨庆勇为论文通讯作者,麻豆 已出站博士后胡悦(现就职于中国农业科学院油料作物研究所),博士研究生贾宇鹏为论文共同第一作者。麻豆 周永明教授、范楚川教授和崖州湾国家实验室青年科学家杨植全给予研究重要支持。该研究获得国家自然科学基金、国家重点研发计划和中央高校基本科研业务费等项目资助,并得到麻豆 作物遗传改良全国重点实验室生物信息学计算平台的支持。
英文摘要:
Abstract
Background
Regulatory elements and their interactions underpin transciptional control and are essential for plant growth and development. Yet, in the allopolyploid crop Brassica napus, the global regulatory landscape and the architecture of its complex regulatory networks remain elusive.
Results
Here we integrate chromatin accessibility and DNA methylation profiles from four representative accessions to generate a comprehensive atlas of 38,068 regulatory elements in Brassica napus. By coupling these regulatory features with expression quantitative trait locus data, we construct a genome-wide regulatory network comprising 24,541 regulatory elements and 791,512 associations between regulatory elements and genes during seed development. Incorporating 3D genome data reveals that spatial proximity promotes co-expression of cross-chromosomal homoeologous gene pairs through putative shared regulatory elements. Moreover, we uncover pronounced subgenome asymmetry, with the regulatory elements on the An subgenome exerting a disproportionately stronger regulatory influence than those on the Cn subgenome.
Conclusions
This study provides valuable resources for studying the intricate regulatory network governed by regulatory elements and sheds new light on exploring the cross-chromosomal regulation in polyploid plants.
审核:杨庆勇
